**文書の過去の版を表示しています。**
rRNA配列を用いた魚種判別、系統樹解析
サンガーシーケンスのデータを開いて、データベースで相同性検索を行い、肉片の魚種を推定する。またシーケンスした配列を含めた系統樹を作成する。
A. 使用するコンピュータについて
今回行う解析はメモリ8GB以上、HDDの空き容量が50GBあるPCであれば十分です。もし十分なスペックのPCが手元にあれば、自分のPCで解析することを推奨します。もし十分なスペックがない場合は、水圏生物工学研究室のPCを遠隔で使用することが可能です。
下記の4つのいずれかの環境を選択し、それぞれ事前準備を進めてください。
以下は「水圏生物工学研究室のLinux PCにログインして解析する」場合を想定して説明しますが、今回使用するソフトウェアはWindows版、Mac版、Linux版それぞれインストーラが存在するので、どのOSを使っても大丈夫です。
B. サンガーシーケンス配列解析、および系統樹作成のプログラムであるGeneiousの体験版をインストール
1.ウェブブラウザ(Firefox)を開く。
2.とりあえず、今見ているこのページをFirefoxで開いておきましょう。皆さんのPCとサーバ間では文字のコピー&ペーストが行えるはずです。
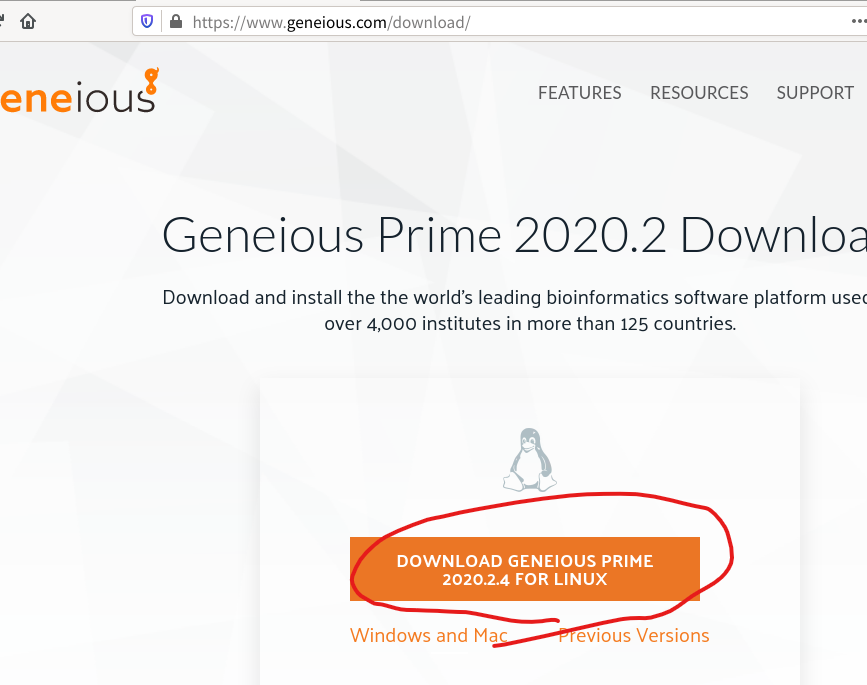
3.Geneiousのインストールファイルをダウンロードする。下記のページの「Download…」ボタンをクリックします。
https://www.geneious.com/download/
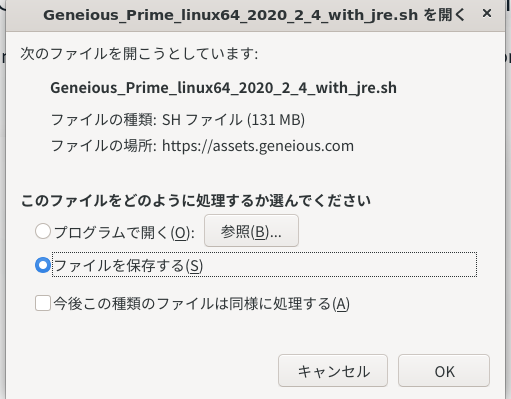
4.「ファイルを保存する」で「OK」を押します。(WindowsやMacの人は、それぞれ適当にファイルを保存したら、ダブルクリックするなりしてインストールを進めてGeneiousを起動し、9.まで進んでください。)
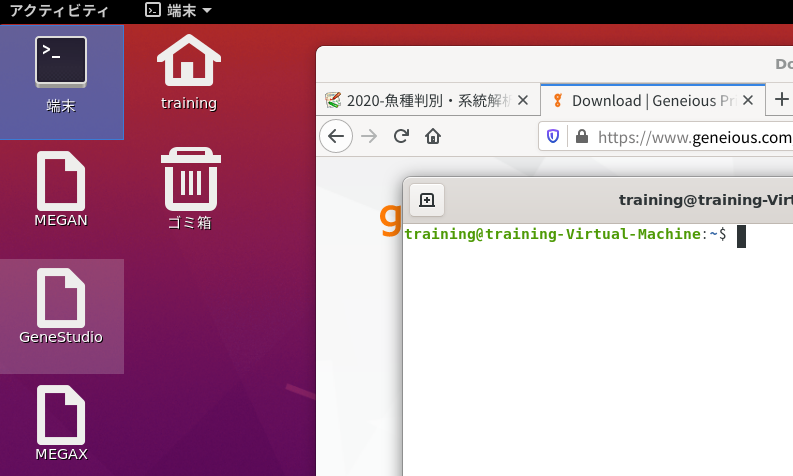
5.デスクトップにある「端末」アイコンをダブルクリックしてターミナルを開きます。
6.ダウンロードしたGeneiousのインストーラを実行するために下記のコマンドを入力します。
#Downloadsフォルダに移動する cd Downloads #ダウンロードしたシェルスクリプトを実行する sh Geneious_Prime_linux64_2020_2_4_with_jre.sh
ターミナルで良く使用するキー、コマンドとしては
・カーソルキーの↑↓でコマンドの履歴を表示する ・Tabキーを押して途中まで入力したコマンド、ファイル名などを補完する ・ls ・・・ 現在のフォルダの中にあるファイル一覧を表示 ・cd ・・・ ディレクトリを移動する ・more / less ・・・ ファイルの中身を表示する
7.Geneiousのインストーラに従ってインストールを行います。
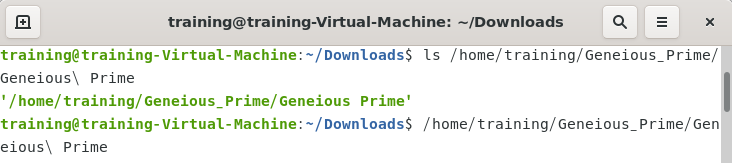
8.Geneiousを起動します。ターミナル上で次のコマンドを入力してください。
/home/training/Geneious_Prime/Geneious\ Prime
9.「Trial Later」をクリックします。
C. データベースで相同性検索を行う
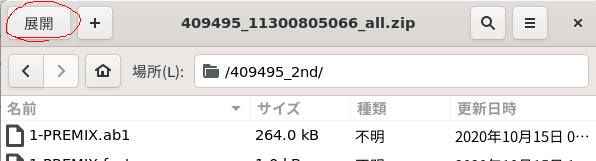
1.下記のzipデータをダウンロードし、アーカイブマネージャーで開いて、「展開」をクリックし、適当な場所にファイルを解凍する。(現在は仮のデータ。XXX.ab1を使えば良い。)
http://www.suikou.fs.a.u-tokyo.ac.jp/yosh/lib/exe/fetch.php?media=409495_11300805066_all.zip
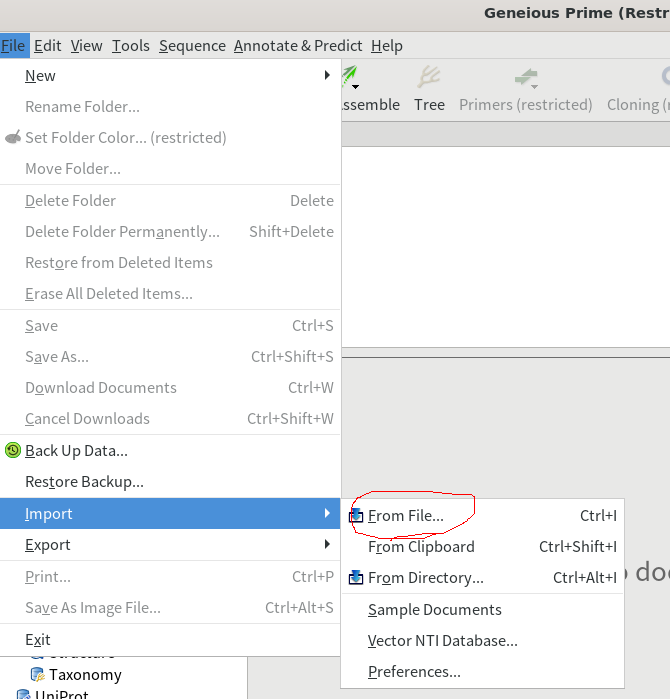
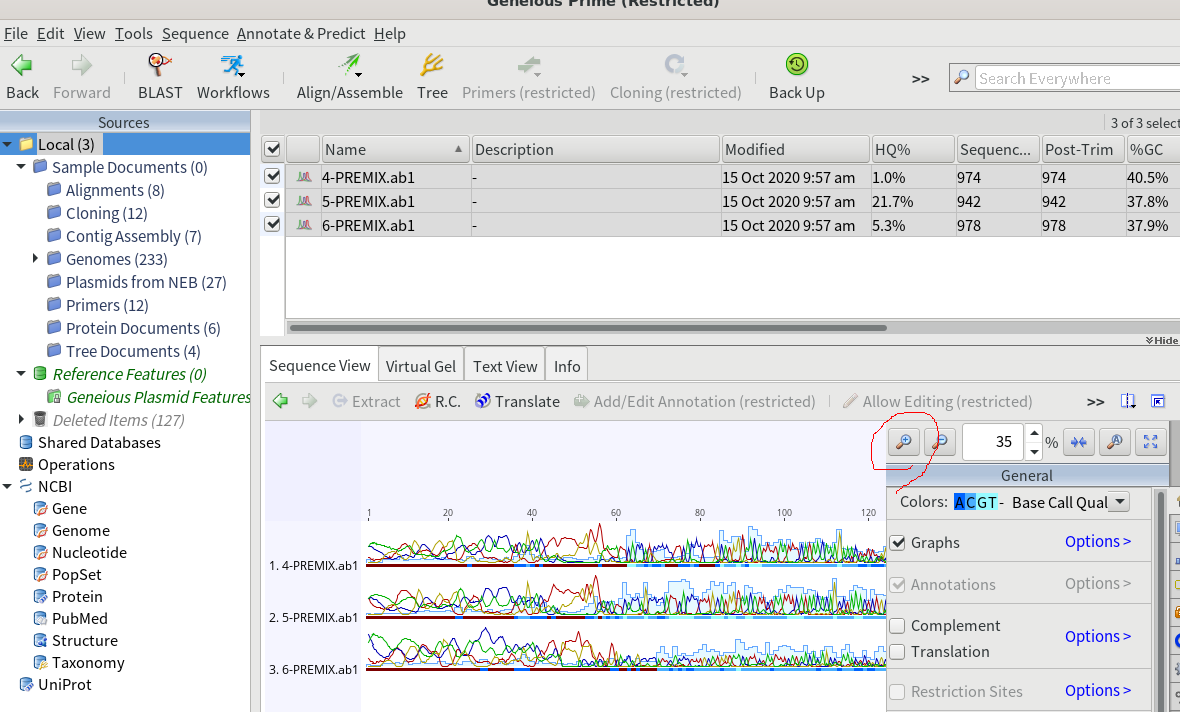
2.Geneiousでシーケンスファイルを開く。「Sources」をLocalなど適当な場所を選択しておいて、「File」→「Import」→「Frome File…」をクリックし、先ほど解凍したシーケンスファイルを選択して、「Import」をクリックする。
3.拡大すると、サンガーシーケンスの波形を見ることが出来る。
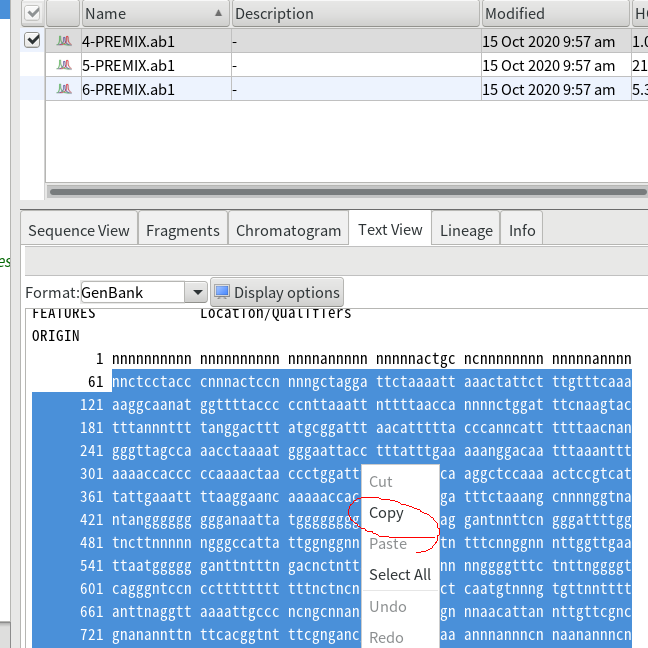
4.シーケンス結果から塩基配列を取得するには、「Text View」を開いて、読めていそうな範囲を選択し、配列を「Copy」する。数字もコピーされてしまうが、この後実行するBlast検索では塩基配列以外の文字列は削除され影響が無いのでそのまま進む。
5.下記のNCBI BLASTのページを開いて、「nucleotide → nucleotide」(通称blastn)を開いて、コピーした配列をクエリーに張り付ける。Databaseにnr/ntが選択されていることを確認して、BLASTをクリックする。nr/ntはGenbankに登録された配列の冗長さを除去した(non-redundantな)データベースで、幅広い生物種・遺伝子が網羅的にバランスよく登録されていて、まずはここで配列を検索する研究者が多い。
https://blast.ncbi.nlm.nih.gov/Blast.cgi
6.そのほか、魚類のミトコンドリア専用のデータベースとして、東大岩崎研で維持されているMitoFishデータベースがある。
http://mitofish.aori.u-tokyo.ac.jp/
こちらは2020年10月現在、2,939種の魚の完全長のミトコンドリアが登録されている。NCBI NTデータベースと、MitoFishデータベース両方で検索して違いを比較する。
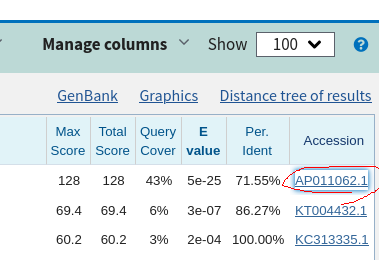
7.ミトコンドリアの配列と、シーケンスデータのアライメント。NCBI、MitoFishどちらも結果を適当にクリックしていると、ヒットした配列のAccession番号のリンクを見つけることが出来るはず。Accession番号を開くと、Genbankに登録されている配列を直接表示することが可能である。
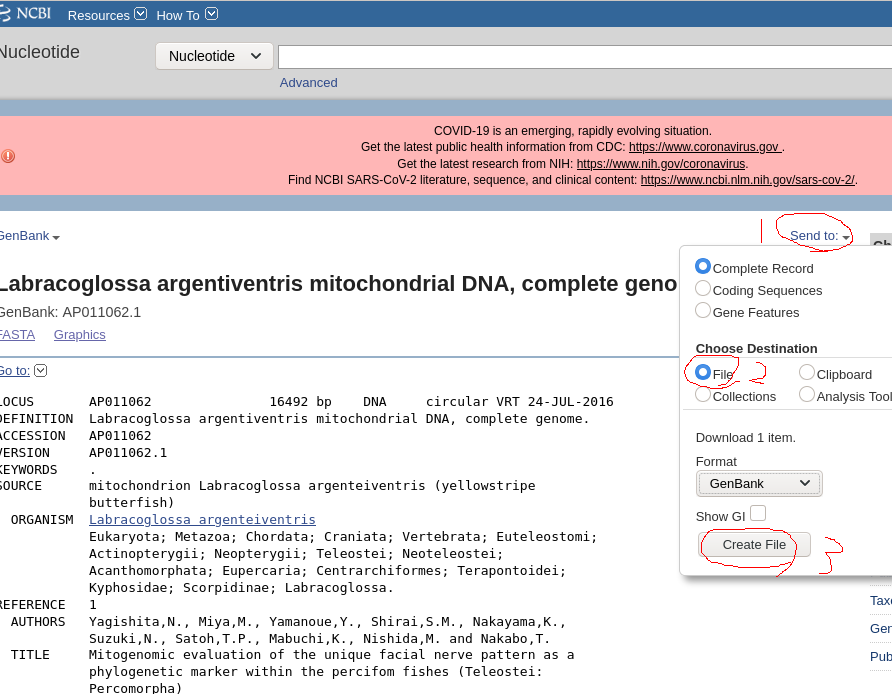
8.シーケンスデータと相同性のある完全長ミトコンドリアの配列をGenbankから探し、GenBank形式でファイルに保存するを選んでダウンロードする。
9.Geneiousで「File」→「Import」→「Frome File…」をクリックし、先ほどダウンロードしたGenBankファイルを開く。
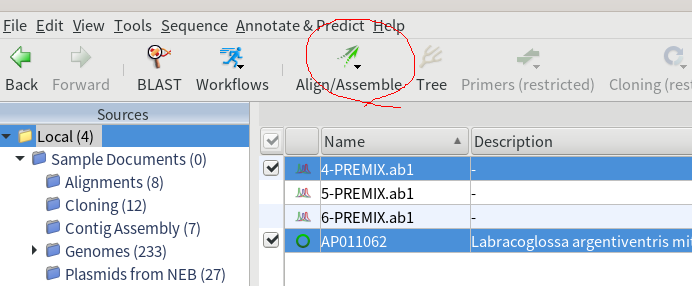
10.シーケンスデータと、インポートしたGenBankファイルを選択し、「Align/Assemble」→「Pairwise Align…」をクリックする。
11.無料版だと、アライメントで高速なMUSCLEなどの外部プログラムが実行できないので、Geneious Alignmentを使用する。Geneious Alignmentには自動で配列の向きを揃えてくれる機能があるので便利。「Automatically determine direction (slower)」にチェックを入れて「OK」を押す。
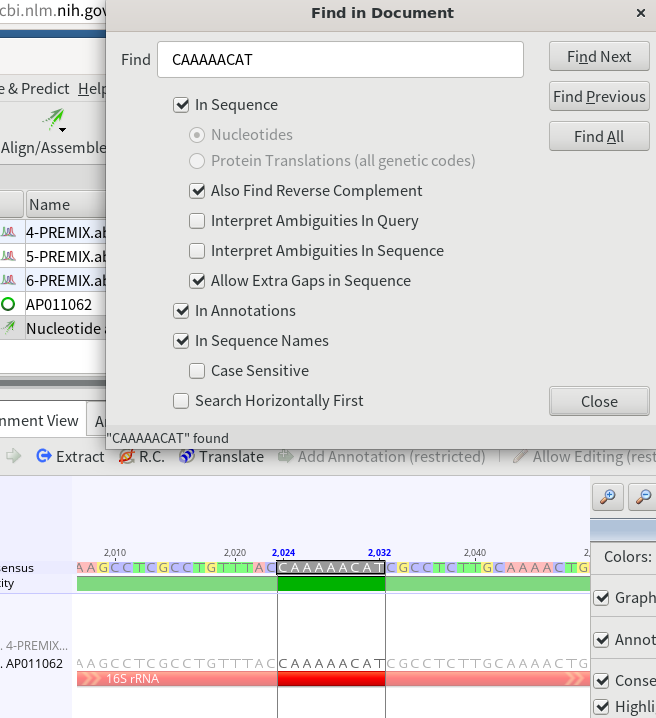
12.Alignment ViewでCtrl+Fを押すと、配列を検索する画面が開くので、下記のプライマーの配列を張り付けて検索してみる。もしヒットしない場合は、プライマーの配列が保存されていない可能性もあるため、適当に検索する配列を短くしてヒットするかどうかを見ていく。ヒットする配列は基本的には16S rRNAの中にあるはずである。
16SarL CGCCTGTTTATCAAAAACAT 16SbrH CCGGTCTGAACTCAGATCACGT
13.プライマーの配列から何塩基くらい離れたところからシーケンスが開始されているか、シーケンスデータとリファレンス配列が不一致な場所があれば、波形が綺麗に読まれているかどうかを確認する。
D. 系統樹作成
ミトコンドリア16S rRNAによる魚類の系統樹を作成し、魚類の中での系統関係を解析する。
1.下記のファイルには46種の生物のミトコンドリア16S rRNA配列が含まれているのでダウンロードする。
http://www.suikou.fs.a.u-tokyo.ac.jp/yosh/lib/exe/fetch.php?media=16s.zip
2.Geneiousの「File」→「Import」→「Frome File…」からダウンロードしたファイルを開く。その際、「Nucleotide sequences」→「Keep sequences separate」を選んでおく。
3.開いた配列を全て選択して、「Align/Assemble」→「Pairwise Align…」をクリックし、マルチプルアライメントを作成する。(しばらく時間がかかる。)
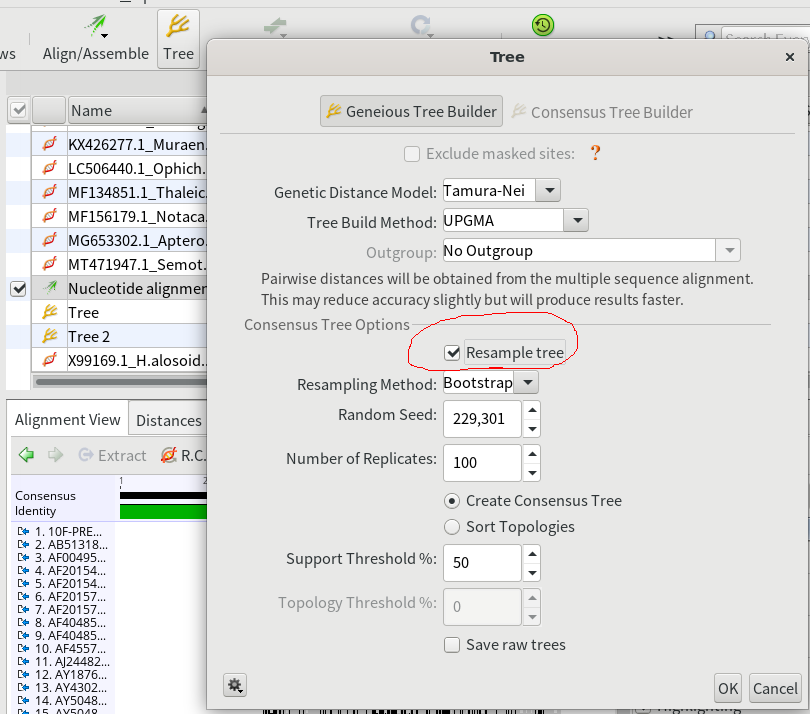
4.マルチプルアライメント結果を選択した状態で、「Tree」をクリックし、UPGMAによる系統樹を作成する。その際各分岐の確からしさをブートストラップ法によって求めるため、「Resample tree」にチェックを入れて「OK」を押す。
5.Genbankに登録された配列の中から、興味のある魚種のミトコンドリア16Sを抽出してGeneiousに取り込み、系統樹を作成する。
https://www.ncbi.nlm.nih.gov/nucleotide/
例えばゼブラフィッシュの16Sを探したい場合は、「Danio rerio 16S complete」などで検索してみる。
作成した系統樹は既知の系統樹と一致するか、一致しない場合は理由を考えてみる。